Nuevas variantes genéticas asociadas a miocardiopatía dilatada adquirida. Hacia un nuevo panel poligénico predisponente
pp. 15-25
DOI:
https://doi.org/10.7775/rac.es.v93.i1.20851Palabras clave:
Miocardiopatìa dilatada , IInsuficiencia cardíaca , Genética , Enfermedad de ChagasResumen
Introducción: La insuficiencia cardíaca con fracción de eyección ventricular izquierda reducida (FEVIr) es una de las patologías cardiovasculares con mayor mortalidad. La existencia de una predisposición genética para el desarrollo de esta patología ante la presencia de una noxa es aún incierta.
Objetivos: El objetivo de este estudio fue identificar asociaciones entre variantes genéticas en alelos polimórficos, polimorfismos de nucleótido único (SNPs) con la presencia de FEVIr y de trastornos de conducción intraventricular (TCIV), en un modelo de miocardiopatía adquirida como es la chagásica.
Material y métodos: Se incluyó como modelo de estudio a pacientes seropositivos para enfermedad de Chagas con data de infección de más de 20 años, un grupo con FEVIr (FEVI ≤35 %) y otro con FEVI preservada, FEVIp (≥50 %). Se realizó una toma de sangre que fue procesada para la obtención del ácido desoxirribonucleico (ADN), que se envió a un laboratorio internacional de genotipado. Se preparó un panel de SNPs de genes utilizando la base internacional The Genome Aggregation Database (GnomAD), eligiendo SNPs con una frecuencia en la población del 10 % al 40 %. Los SNPs elegidos están relacionados con genes responsables del proceso de contracción y relajación ventricular (TTN, BAG3, MTSS1), el metabolismo miocárdico (PPARGC1A, SIRT1, AKT1 mTOR, AMPK), receptor adrenérgico beta 1 (ADRB1), receptor colinérgico muscarínico 2 (CHRM2), receptor de angiotensina II tipo 1 (AGTR1B), y el péptido natriurético auricular (NPPA) Mediante diversos modelos de inteligencia artificial para aprendizaje supervisado (Regresión Logística, Máquinas de Vectores de Soporte, Redes Neuronales Artificiales, Naive Bayes, Árboles de Clasificación y Random Forest) se evaluaron 68 SNPs como predictores de la presencia de dos fenotipos: FEVIr, y TCIV. El desempeño de los modelos para la predicción de la FEVIr se evaluó mediante la técnica de validación cruzada (cross-validation), con la métrica F1 como medida de precisión para seleccionar el mejor modelo.
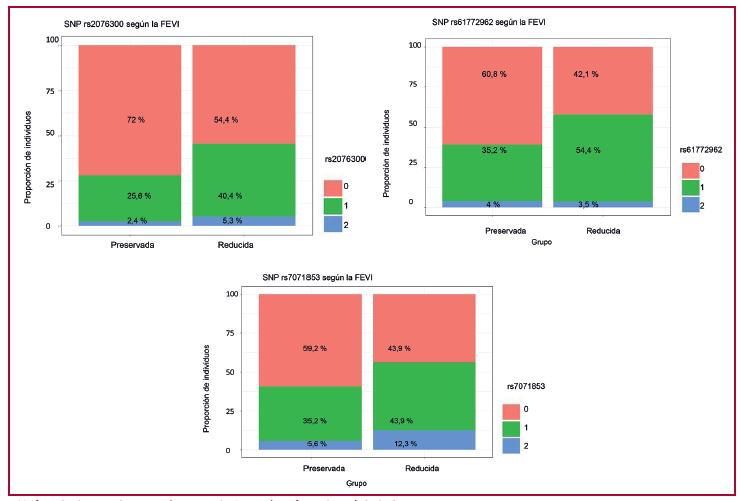
Resultados: Se incluyeron 182 pacientes, con una mediana de edad de 62 años, el 39,6 % hombres. El 31 % presentó FEVIr y el 53 % algún TCIV. El modelo con el mejor desempeño fue la regresión logística (F1 = 0,85), por lo que se la utilizó para expresar la asociación mediante el Odds Ratio y su IC del 95%. Se observó que las variantes rs2076300, rs61772962 y rs7071853 fueron predictores independientes de reducción de la FEVI. Mientras que, para la presencia de TIVC, el único predictor fue el SNP rs72840788. El SNIP rs61772962 corresponde al gen PRKAA2, que codifica a la subunidad catalítica alfa-2 de la proteína quinasa activada por 5’-AMP. Por su parte el rs7071853 y el rs72840788 corresponden al gen que codifica a la proteína BAG3 (regulador 3 de chaperona). Finalmente el SNP rs2076300 corresponde al gen DSP que codifica una desmoplaquina, proteína de la placa de unión de los desmosomas.
Conclusiones: En este modelo de derivación, en un conjunto de pacientes con serología positiva para Chagas se identificaron 3 SNPs predictores de reducción de la FEVIr y un SNP predictor de TCIV. La reproducibilidad de estos resultados debería ser confirmada en un modelo de validación con una mayor muestra de individuos. Además, este hallazgo podría ser de utilidad en miocardiopatías dilatadas de otras etiologías.
Descargas
Publicado
Número
Sección
Licencia
Derechos de autor 2025 Revista Argentina de Cardiología

Esta obra está bajo una licencia internacional Creative Commons Atribución-NoComercial-CompartirIgual 4.0.













